2. 西藏农牧科学院畜牧兽医研究所, 拉萨 850009
2. Institute of Animal Science, Tibet Academy of Agricultural and Animal Husbandry Sciences, Lhasa 850009, China
藏山羊作为我国独特的种质资源,其体型矮小,被毛富有光泽,颜色较杂,除白色和黑色较多外,还有青色、褐色等,在青藏高原的农业、经济和文化,甚至宗教等方面都扮演了重要角色[1],品种主要分布在西藏自治区全境、四川省甘孜和阿坝2个自治州、青海省玉树和果洛藏族自治州、甘肃甘南藏族自治州及新疆部分地区[2]。高原环境的长期阻隔以及地理分布的差异,在长期的自然选择和人工选择下,藏山羊群体间缺乏足够的基因交流,逐步形成了不同的生态类群。王杰等[3]、王永等[1]先后采用SSR与ISSR分子标记对藏山羊的遗传多态性进行了分析,结果显示,藏山羊多样性较丰富,但群体间存在差异。在此次采样过程中,笔者发现当地牧民大多以单户养殖为主,一些产区(如城关镇、林周县、萨嘎县等)的藏山羊群体数量已经极其稀少。加上近年来,在经济利益的驱动下,各地也持续引入外来山羊品种,如辽宁绒山羊[4]、南江黄羊[5-6]、内蒙古白绒山羊[7]等对本地山羊品种进行遗传改良,提高其综合生产性能,导致藏山羊这一遗传资源正在面临危机。
线粒体基因组(Mitochondrial DNA,mtDNA)上的细胞色素b(Cytb)是蛋白编码基因之一,其进化速度适中,序列片段包含种内到种间的进化遗传信息,已被用来研究多个物种的系统发育关系和遗传多样性[8-9]。然而,利用Cytb基因对藏山羊的遗传多样性和分子进化方面的研究还未见报道。本研究对西藏地区8个群体共157个藏山羊个体的Cytb基因全序列进行扩增和测序,在此基础上分析群体遗传多样性,揭示不同地域藏山羊群体间的遗传结构及系统发育关系,为藏山羊品种资源的保护与利用提供理论参考。
1 材料与方法 1.1 样本采集根据藏山羊的主产地区,从西藏8个地区采集藏山羊血液样本共计157个,每个群体内的个体之间无亲缘关系。采用颈静脉采血,3.9% ACD抗凝,-20 ℃冰箱储存备用。样本详细信息见表 1。
|
|
表 1 藏山羊样品采集信息 Table 1 Sample information of Tibetan goats |
采用DNA提取试剂盒(TIANamp Genomic DNA Kit;北京)提取藏山羊血液基因组DNA。扩增Cytb全序列所用引物参照藏山羊mtDNA全序列(GenBank No.:KJ940969)设计(正向引物F1:5′-AATAGGCGAAGGTTTTGAA-3′,反向引物R1:5′-GCTTTGGGTGCTGATAGTG-3′),并由成都擎科生物公司合成。本研究中,PCR为30 μL反应体系:10×缓冲液15 μL,DNA(2.5 ng·μL-1)1 μL,正反向引物(10 pmol·μL-1)各1 μL,超纯水12 μL。PCR扩增条件:94 ℃预变性5 min,35个循环(95 ℃ 30 s,55.3 ℃ 30 s,72 ℃ 90 s),72 ℃延伸10 min,之后于4 ℃保存。PCR产物在1.5%的琼脂糖凝胶电泳及核酸检测仪上检测纯度及浓度后,送至成都擎科生物有限公司进行测序。为确保序列的准确性,每条序列均经过正反双向测定。
1.2.2 数据处理及分析所有测得并经拼接的DNA序列用DNASTAR软件中的SeqMan 5.01(DNAstar Inc;Madison. WI)程序排列同源序列,并进行人工校正。用DnaSP 5.0软件[10]统计单倍型种类,计算核苷酸多样度(Nucleotide diversity, Pi)和单倍型多样性(Haplotypic diversity, Hd)。用MEGA 4.0软件[11]计算变异位点、简约信息位点、遗传距离等,构建系统发育邻接树(Neighbor-Joining,NJ),以Bootstrap 1 000次重复抽样检验分支置信度[12]。利用Network 4.6.1.0软件[13]构建单倍型网络图,以直观揭示单倍型之间的亲缘关系以及基因流。Arlequin 3.5软件[14]计算群体间遗传分化指数(FST),并根据Nm≈(1-FST)/(2FST)计算群体间的基因流值;将种群进行群体划分模式检测,用分子变异分析方法(AMOVA)估测遗传变异在种群内和种群间的分布、分化指数和对应的P值。
2 结果 2.1 藏山羊的Cytb序列特征及遗传多样性序列扩增及测序后经软件比对并人工校正后得到157条全长1 140 bp的Cytb基因序列(图略),共检测到33个变异位点,包含21个简约信息位点和12个单碱基替换,其中错义突变9个,无义突变24个,所有序列没有出现插入或缺失的变异位点。基于此定义了30种单倍型(H1~H30),其中CG(H1、H2)与LS(H15、H16)为群体独享单倍型。遗传多样性结果表明(表 2),LZ(Hd=0.722±0.097,Pi=0.001 8±0.000 6)与CG(Hd=0.625±0.093,Pi=0.001 8±0.000 4)的多样性指数接近,且高于其他群体;JL多样性指数(Hd=0.133±0.112,Pi=0.000 4±0.000 3)在8个群体中最低。但总的Hd(0.736±0.035)和Pi(0.001 8±0.000 2)值显示出较高水平,表明所研究西藏地区的8个藏山羊群体具有较丰富的遗传多样性。
|
|
表 2 藏山羊群体间遗传多样性指数及中性检验值 Table 2 Genetic diversity and neutrality tests among Tibetan goat populations |
群体间遗传分化指数(Pairwise FST)结果显示(表 3,下三角),78.6 %群体间的FST值达到了显著水平(P < 0.05),表明大部分群体间(22/28,78.6%)发生了显著或极显著的遗传分化。其中CG与LS间差异最大(FST=0.883 0,P < 0.01),表明两组群体间的遗传分化程度最高;反之DX和SG群体间分化程度最低(FST=0.032 9,P>0.05)。基因流参数值(Nm)区间为0.066 3~14.697 6(表 3,上三角),表明各群体之间的基因交流水平差异较大,其中CG、LS与其他群体间的基因交流受阻(Nm < 1),表明群体间高度分离;SG和DX间基因交流较多(Nm>1),群体分化程度低,与遗传分化指数分析结果相符。AMOVA分析结果(FSC=0.392,P < 0.001,表 4)表明,组内群体间遗传分化差异极显著,但变异来源所占比例较低,变异主要发生在种群内部,提示群体遗传结构差异在缩小。整体群体间基因流Nm=0.776 < 1,表明藏山羊整体基因流水平较低,存在一定的遗传分化。
|
|
表 3 藏山羊群体间的遗传分化指数FST(下三角)和基因流值Nm(上三角) Table 3 The pairwise FST(below the diagonal) and gene flow Nm (above the diagonal) among the Tibetan goat populations |
|
|
表 4 藏山羊群体分子变异方差分析 Table 4 Analysis of molecular variance (AMOVA) of Tibetan goat populations |
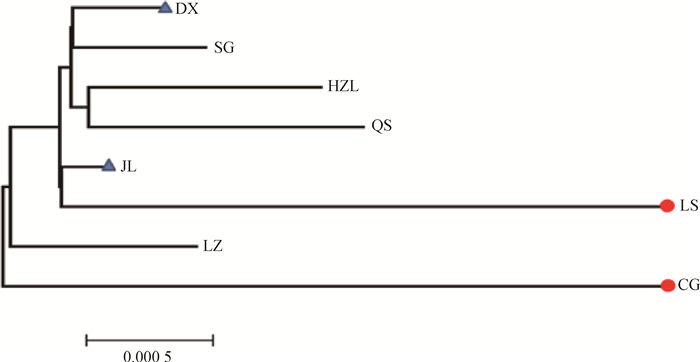
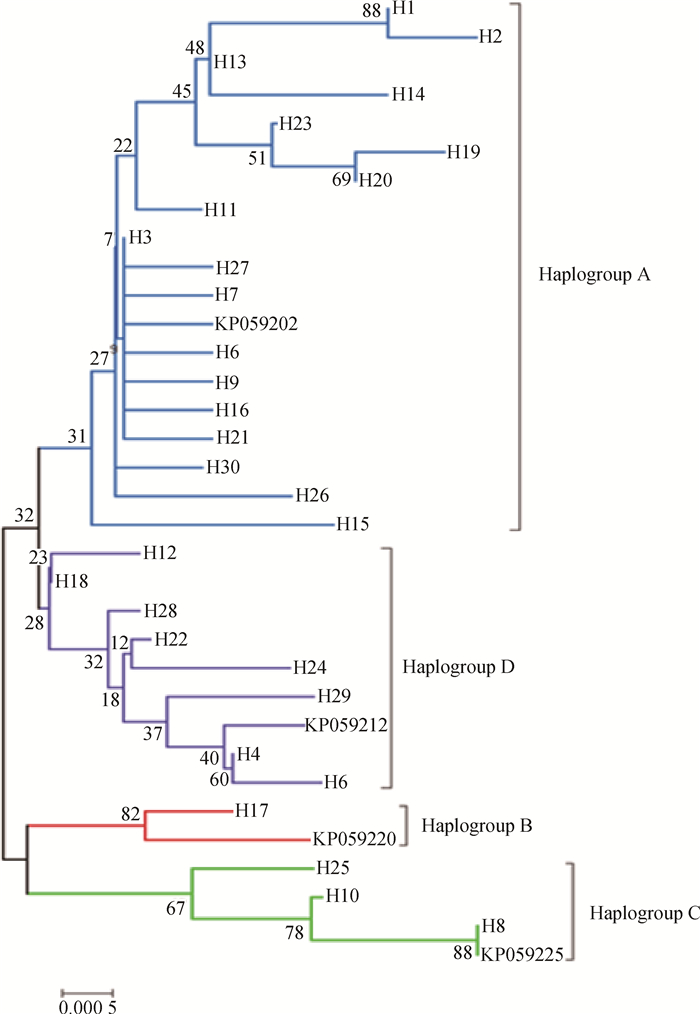
图 1是基于群体间遗传距离构建的群体间NJ树,结果显示,DX与SG首先聚在一起,之后依次与HZL、QS、JL、LS、LZ、CG聚类。总体上看,CG与LS的遗传关系最远,DX与JL遗传关系最近。另外,将NCBI下载的山羊Cytb 4个单倍型组(Haplogroup A-D,登录号:KP059202、KP059212、KP059220和KP059225)作为参考序列,构建了30种单倍型系统发育NJ树(图 2),藏山羊单倍型聚为4个支系,呈现出较强的谱系结构,不同地理来源的个体没有完全形成各自的分支,而是混杂分布部分交错,没有形成明显的地理分隔格局。其中,Haplogroup A是主要单倍型组,由8个群体单倍型组成,其中LS、CG和JL的单倍型只在A系;Haplogroup B构成最简单,只有1种单倍型(H17);Haplogroup C由来自QS和HZL的部分单倍型组成;Haplogroup D由HZL、QS、SG和DX的部分单倍型组成。
|
图 1 基于藏山羊群体间遗传距离构建的亲缘关系NJ树 Figure 1 An neighbor-joining (NJ) tree based on genetic distance of the Tibetan goat populations |
|
图 2 藏山羊单倍型系统发育NJ树 Figure 2 An neighbor-joining (NJ) tree based on Tibetan goat haplotypes |
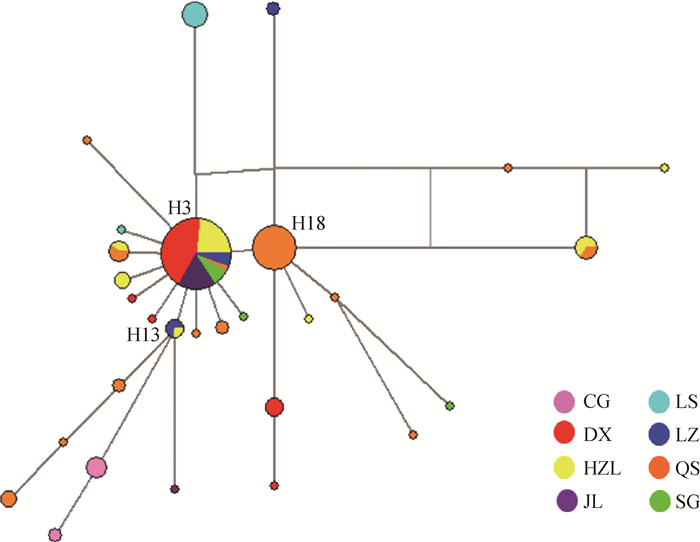
根据30种单倍型序列数据及其出现的频率,绘制出藏山羊群体单倍型的中介网络图。图 3显示,以H3为中心,呈星状向周围单倍型发散,表明群体可能发生过群体扩张;其次,H3与H18和H13连接,逐渐形成大大小小的网络分支,推断H3是主导单倍型,主要形成H3-H18和H3-H13的2个不重叠分布区的历史基因流,通过扩散或基因交流,衍生出其余单倍型,分布于不同群体中;其中QS经过基因流的扩散,分布最广。部分来自不同地区的群体的个体分享同种单倍型,但地理位置相同或相近的个体不完全聚类到同一个分支,表现了藏山羊群体地理关联性较弱。
|
图 3 藏山羊单倍型中介网络图 Figure 3 Network analysis of Tibetan goat haplotypes |
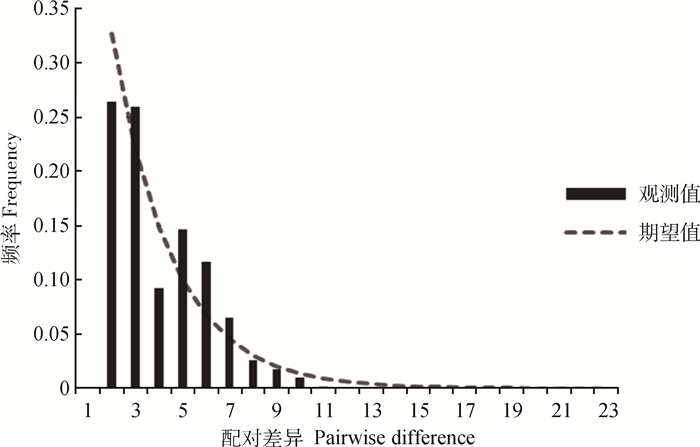
中性检验值分析显示(表 2),从单个地理群体看,JL、SG、LS的Tajima’s D和Fu’s Fs值为一正一负,说明3个群体符合中性假说,没有发生过群体扩张事件。DX、LZ的2个值均为正,提示在历史发展中,群体数量有过缩减;CG、HZL、QS的2个值均为负数,表明群体数量可能发生过急速扩增。从整体藏山羊种群来看,其中性检验结果均为负值(Tajima’s D=-1.900,P < 0.05;Fu’s Fs=-22.020,P < 0.01),且错配分布曲线显示为多峰现象(图 4),表明藏山羊在历史驯养过程中,可能因为部分种群的急速扩增而导致整体有种群扩增的迹象,曲线的多峰现象同时也验证了部分群体数量的缩减事件。
|
图 4 基于Cytb基因分析藏山羊群体的错配分布曲线 Figure 4 Mismatch distribution curves of the Tibetan goats based on Cytb sequences |
普遍认为,遗传多样性的高低反映了群体的环境适应能力和进化潜能[15]。本研究中,157只藏山羊共有30种单倍型,整体单倍型多样性显示出较高水平(0.736),表明整个藏山羊群体较丰富的遗传多样性。但各群体的单倍型多样性水平参差不齐,低至0.133,高达0.722,核苷酸多样度均为较低水平,表明群体间多样性水平差异较大,然而最高多样性参数值(林周藏山羊群体LZ)低于中国家养山羊地方品种的平均水平[16-17]。此外,中性检验结果和错配分析证明,在藏山羊历史驯养过程中经历过群体扩张事件,表明群体遗传变异得到了积累,整体表现出较高的多样性。然而值得注意的是,如果一个群体长期处于低水平的变异率或遗传多样性的状态下,这将成为一个重要的濒危信号[18]。吉隆县位于西藏自治区西南部,是西藏同纬度地带自然条件比较独特的地区之一,自然生态环境结构复杂,交通相对闭塞,这些因素可能导致吉隆藏山羊群体(JL)与外部群体基因交流受限,有效群体数量逐渐缩小,处于多样性快速丢失的过程中。因此,保护藏山羊群体的遗传多样性已刻不容缓。
3.2 藏山羊群体的遗传结构FST值的大小反映了给定群体间的遗传分化水平,0~0.05表示轻度分化,0.05~0.25表示中度分化,大于0.25表示重度分化。本研究中,8个群体间遗传结构大部分有了明显分化,但分化程度有所不同。AMOVA结果显示了群体间极显著的变异程度,但变异来源所占的比例较低,提示群体间的遗传结构差异正在缩小。Nm值大小表明一个群体向另一个群体的基因流动,城关群体(CG)与拉萨群体(LS)的单倍型种类完全独立,不与其他群体共享,且基因流值均小于1,表明城关地区和拉萨地区的藏山羊群体分离程度最高。这与我们之前基于mtDNA D-loop序列所研究的藏山羊遗传结构结果是相符的[19]。产生此结果的一个重要原因可能是,所研究群体的有效群体数量较低(如LZ、SG、CG等),且生活在封闭的高山环境中,导致当地藏山羊与邻近藏山羊群体之间的基因交流受限,进而长期保持低水平种群规模。由于有效群体数量的衰退,核苷酸替换数也极大可能被固定[20-21]。近年来,随着山羊养殖业的迅速发展,牧民为了短期效益,盲目地引入外来品种与藏山羊进行无序杂交,进一步导致藏山羊优良基因逐渐丢失,多样性降低,遗传结构差异缩小,地理分隔格局变弱。结合J.C.Avise等[22]提出的亲缘地理格局的模式分析藏山羊8个群体的遗传结构,LS和CG符合“岛屿模型”,出现独享单倍型;QS、DX、HZL、LZ、JL和SG地理屏障作用较小,使群体未彼此隔开,个体发生过相互迁移,有较多的基因交流。其中,当雄县位于西藏自治区中部,为拉萨市的纯牧业县,加上现代畜牧科技(如人工授精技术)的利用与推广,使得当雄产区的藏山羊与外群基因交流更为充分,群体间遗传分化变弱。
3.3 藏山羊群体的多个母系起源西藏卡若遗址出土的野生动物骨骼里发现了藏原羊的骨骼[23],说明藏族先民驯养家羊的历史可追溯至4 000年前的新石器时期。迄今为止,关于藏山羊起源的观点并不一致。在以往的研究中,B. Fan等[24]分析了13个中国山羊品种的mtDNA D-loop序列多样性,王杰等[3]利用微卫星标记分析了藏山羊群体系统发育关系,其结果均表明,藏山羊可能有多个母系起源;此外,蔡欣等[25]得到了不一致的结果,提出了藏山羊单个起源的观点,可能是由于样本采集地点、数目差异等因素导致。目前,对家养山羊的起源研究大部分是通过对mtDNA的研究将山羊大致分为了以下几个单倍型组:Haplogroup A、B、C[26]、D[27]、F[28]和G[29]。M.B.Joshi等[30]命名了一个新的单倍型组(Haplogroup E),但在加大样本量研究后,Haplogroup E被认为是A的附系[31],现今我国家养山羊共发现了4个支系[32],在本研究中也证实了这点。本研究加入NCBI下载的4种Cytb单倍型作为参考序列构建藏山羊30个单倍型系统发育树,形成4个主要的单倍型组(Haplogroup A-D),其中Haplogroup A为主要单倍型组,Haplogroup B只由LZ一种单倍型构成,结果提示,藏山羊有4个母系起源,这与已发表的藏山羊起源研究的结果是一致的[19],进一步支撑了藏山羊多个起源的假说。Haplogroup A广泛分布于全世界家养山羊品种中,有报道称Haplogroup B起源于中国[33],Haplogroup C现在主要分布在欧洲地区,K.Nomura等[34]研究表明,Haplogroup D主要分布在亚洲南部和中部地区。本研究结果表明,藏山羊可能起源于欧亚大陆,有4个母系起源。此外,藏山羊个体没有完全依据采样区域形成独立分支,而是呈现出地理上的融合,这一点在Haplogroup A中有明显体现,8个群体中均有单倍型出现在Haplogroup A,Haplogroup C和D也有部分区域混合。Haplogroup B的构成单倍型最少,可能是因为样本数不够,需要更多的样本支持。网络图中心单倍型H3的主要群体有DX和HZL,表明这2个群体古老单倍型保留得最多,分布最广。此外,曲水地区的藏山羊群体传播范围广,在进化上处于更近的时期。这样的分布现况可能是多个母系祖先的影响、世代重叠、不同地理位置的群体混合,以及伴随着基因漂变、自然选择等原因导致[35]。
4 结论本研究表明,8个藏山羊群体总的遗传多样性水平较高,但群体间的遗传多样性水平不一,差距较大。各群体间大部分发生了明显的遗传分化,但没有形成明显的地理分隔格局;8个藏山羊群体分成了A、B、C、D 4个单倍型组,提示藏山羊有4个母系起源。
| [1] |
王永, 王杰, 许期树, 等. 西藏日土藏山羊ISSR标记遗传多态性研究[J]. 畜牧兽医学报, 2010, 41(9): 1208–1212.
WANG Y, WANG J, XU Q S, et al. Analysis of genetic diversity in Ritu Tibetan goats by ISSR[J]. Acta Veterinaria et Zootechnica Sinica, 2010, 41(9): 1208–1212. (in Chinese) |
| [2] |
秦国庆, 常洪. 藏山羊遗传资源及利用状况[J]. 中国养羊, 1997(4): 3–5.
QIN G Q, CHANG H. Genetic resources and utilization of Tibetan goats[J]. China Herbivores, 1997(4): 3–5. (in Chinese) |
| [3] |
王杰, 华太才让, 欧阳熙, 等. 藏山羊微卫星DNA多态性研究[J]. 中国草食动物, 2006(S1): 122–126.
WANG J, HUATAI C R, OUYANG X, et al. Study on microsatellite DNA polymorphism of Tibetan goats[J]. China Herbivores, 2006(S1): 122–126. (in Chinese) |
| [4] |
文淑义, 王秋福, 王德元, 等. 辽宁绒山羊适应性观察及与藏山羊杂交试验报告[J]. 四川草原, 1995(4): 42–48.
WEN S Y, WANG Q F, WANG D Y, et al. Adaptive observation of Liaoning cashmere goats and a report on hybrid experiment with Tibetan goats[J]. Journal of Sichuan Grassland, 1995(4): 42–48. (in Chinese) |
| [5] |
任称罗尔日, 周光领, 周炬钟, 等. 南江黄羊与藏山羊杂交的效果分析[J]. 四川畜牧兽医, 2000, 27(S1): 59–60, 62.
RENCHEN L E R, ZHOU G L, ZHOU J Z, et al. Heterosis analysis of crossing Nanjiang yellow goats with Tibetan goats[J]. Sichuan Animal & Veterinary Sciences, 2000, 27(S1): 59–60, 62. (in Chinese) |
| [6] |
王燕军, 张月欢, 肖文平. 丹巴县引进南江黄羊杂交改良本地藏山羊的实践[J]. 中国畜牧兽医文摘, 2015, 31(4): 57.
WANG Y J, ZHANG Y H, XIAO W P. The practice of introducing the Nanjiang yellow goat in Danba County to improve local Tibetan goats[J]. Chinese Abstract of Animal Husbandry and Veterinary Medicine, 2015, 31(4): 57. (in Chinese) |
| [7] |
郭淑珍, 马登录, 牟永娟, 等. 内蒙古白绒山羊及其与藏山羊杂交后代在甘南州的适应性观察[J]. 中国草食动物, 2008, 28(3): 38–40.
GUO S Z, MA D L, MOU Y J, et al. The adaptive observation of Mongolia white cashmere goat and its hybrid offspring with Tibetan goat in Gannan[J]. China Herbivores, 2008, 28(3): 38–40. (in Chinese) |
| [8] | RAMÍREZ J D, DUQUE M C, GUHL F. Phylogenetic reconstruction based on Cytochrome b (Cytb) gene sequences reveals distinct genotypes within Colombian Trypanosoma Cruzi Ⅰ populations[J]. Acta Trop, 2011, 119(1): 61–65. DOI: 10.1016/j.actatropica.2011.04.009 |
| [9] | LIU J, WANG C M, FU D L, et al. Phylogeography of Nanorana parkeri (Anura:Ranidae) and multiple refugia on the Tibetan Plateau revealed by mitochondrial and nuclear DNA[J]. Sci Rep, 2015, 5: 9857. DOI: 10.1038/srep09857 |
| [10] | LIBRADO P, ROZAS J. DnaSP v5:a software for comprehensive analysis of DNA polymorphism data[J]. Bioinformatics, 2009, 25(11): 1451–1452. DOI: 10.1093/bioinformatics/btp187 |
| [11] | TAMURA K, DUDLEY J, NEI M, et al. MEGA4:Molecular Evolutionary Genetics Analysis (MEGA) software version 4.0[J]. Mol Biol Evol, 2007, 24(8): 1596–1599. DOI: 10.1093/molbev/msm092 |
| [12] | SANDERSON M J. Confidence limits on phylogenies:the bootstrap revisited[J]. Cladistics, 1989, 5(2): 113–129. DOI: 10.1111/cla.1989.5.issue-2 |
| [13] | BANDELT H J, FORSTER P, RÖHL A. Median-joining networks for inferring intraspecific phylogenies[J]. Mol Biol Evol, 1999, 16(1): 37–48. DOI: 10.1093/oxfordjournals.molbev.a026036 |
| [14] | EXCOFFIER L, LISCHER H E L. Arlequin suite ver 3.5:a new series of programs to perform population genetics analyses under Linux and windows[J]. Mol Ecol Resour, 2010, 10(3): 564–567. DOI: 10.1111/men.2010.10.issue-3 |
| [15] | LIU J B, DING X Z, ZENG Y F, et al. Genetic diversity and phylogenetic evolution of Tibetan sheep based on mtDNA D-loop sequences[J]. PLoS One, 2016, 11(7): e0159308. DOI: 10.1371/journal.pone.0159308 |
| [16] |
黄勤华, 刘若余, 吴芸, 等. 贵州4个山羊群体mtDNA Cytb基因多态性研究[J]. 中国畜牧杂志, 2010, 46(1): 4–7.
HUANG Q H, LIU R Y, WU Y, et al. Study on polymorphism of cytochrome b gene in four Guizhou goat breeds[J]. Chinese Journal of Animal Science, 2010, 46(1): 4–7. (in Chinese) |
| [17] |
黄勤华, 刘若余, 邓书堪. 贵州白山羊与湖南马头山羊mtDNA Cytb基因系列比较及系统进化研究[J]. 安徽农业科学, 2009, 37(25): 11897–11899.
HUANG Q H, LIU R Y, DENG S K. Comparison and Systematic evolution study of cytochrome b gene (Cytb) between Guizhou white goat and Hunan Matou goat[J]. Journal of Anhui Agricultural Sciences, 2009, 37(25): 11897–11899. DOI: 10.3969/j.issn.0517-6611.2009.25.027 (in Chinese) |
| [18] | LI L, ZHANG J, ZHU J Q, et al. Genetic diversity of nine populations of the black goat (Capra hircus) in Sichuan, PR China[J]. Zoolog Sci, 2006, 23(3): 229–234. DOI: 10.2108/zsj.23.229 |
| [19] | DENG J, FENG J, LI L, et al. Polymorphisms, differentiation, and phylogeny of 10 Tibetan goat populations inferred from mitochondrial D-loop sequences[J]. Mitochondr DNA, 2017: 1–7. |
| [20] | KIMURA M. On the probability of fixation of mutant genes in a population[J]. Genetics, 1962, 47(6): 713–719. |
| [21] | NEI M, MARUYAMA T, CHAKRABORTY R. The bottleneck effect and genetic variability in populations[J]. Evolution, 1975, 29(1): 1–10. |
| [22] | AVISE J C, ARNOLD J, BALL R M, et al. Intraspecific phylogeography:the mitochondrial DNA bridge between population genetics and systematics[J]. Annu Rev Ecol Syst, 1987, 18: 489–522. DOI: 10.1146/annurev.es.18.110187.002421 |
| [23] | WANG Y, WANG J, ZI X D, et al. Genetic diversity of Tibetan goats of plateau type using microsatellite markers[J]. Archiv Tierzucht, 2011, 54(2): 188–197. |
| [24] | FAN B, CHEN S L, KIJAS J H, et al. Phylogenetic relationships among Chinese indigenous goat breeds inferred from mitochondrial control region sequence[J]. Small Rumin Res, 2007, 73(1-3): 262–266. DOI: 10.1016/j.smallrumres.2006.12.007 |
| [25] |
蔡欣, 泽让东科, 苟兴能, 等. 川渝黔地区山羊起源于A和B两母系遗传谱系[J]. 四川大学学报:自然科学版, 2012, 49(4): 887–894.
CAI X, TSERANG D M, GOU X N, et al. Goats from Sichuan, Chongqing and Guizhou were originated from A and B maternal lineages[J]. Journal of Sichuan University:Natural Science Edition, 2012, 49(4): 887–894. (in Chinese) |
| [26] | LUIKART G, GIELLY L, EXCOFFIER L, et al. Multiple maternal origins and weak phylogeographic structure in domestic goats[J]. Proc Natl Acad Sci U S A, 2001, 98(10): 5927–5932. DOI: 10.1073/pnas.091591198 |
| [27] | SULTANA S, MANNEN H, TSUJI S. Mitochondrial DNA diversity of Pakistani goats[J]. Anim Genet, 2003, 34(6): 417–421. DOI: 10.1046/j.0268-9146.2003.01040.x |
| [28] | SARDINA M T, BALLESTER M, MARMI J, et al. Phylogenetic analysis of Sicilian goats reveals a new mtDNA lineage[J]. Anim Genet, 2006, 37(4): 376–378. DOI: 10.1111/age.2006.37.issue-4 |
| [29] | NADERI S, REZAEI H R, POMPANON F, et al. The goat domestication process inferred from large-scale mitochondrial DNA analysis of wild and domestic individuals[J]. Proc Natl Acad Sci U S A, 2008, 105(46): 17659–17664. DOI: 10.1073/pnas.0804782105 |
| [30] | JOSHI M B, ROUT P K, MANDAL A K, et al. Phylogeography and origin of Indian domestic goats[J]. Mol Biol Evol, 2004, 21(3): 454–462. |
| [31] |
武艳平. 中国部分山羊品种多样性及系统进化分析[D]. 北京: 中国农业科学院, 2008.
WU Y P. Diversity and phylogenetic relationships of some Chinese goat breeds[D]. Beijing: Chinese Academy of Agricultural Sciences, 2008. (in Chinese) http://cdmd.cnki.com.cn/Article/CDMD-82101-2008130443.htm |
| [32] | LIU R Y, YANG G S, LEI C Z. The genetic diversity of mtDNA D-loop and the origin of Chinese goats[J]. Acta Genet Sin, 2006, 33(5): 420–428. DOI: 10.1016/S0379-4172(06)60069-3 |
| [33] | LI M. New evidence discovery for maternal lineage B of goats (Capra hircus) in Chinese tropical zone[J]. Geophys Res Lett, 2013, 28(24): 4525–4528. |
| [34] | NOMURA K, YONEZAWA T, MANO S, et al. Domestication process of the goat revealed by an analysis of the nearly complete mitochondrial protein-encoding genes[J]. PLoS One, 2013, 8(8): e67775. DOI: 10.1371/journal.pone.0067775 |
| [35] | ZHAO Y J, ZHANG J H, ZHAO E H, et al. Mitochondrial DNA diversity and origins of domestic goats in southwest China (Excluding Tibet)[J]. Small Rumin Res, 2011, 95(1): 40–47. DOI: 10.1016/j.smallrumres.2010.09.004 |



